traduction: Maugou relecture: Ouser
L'équipe de recherche de FightAIDS@Home teste de nouvelles méthodes de simulation
Par l'équipe de recherche de FightAIDS@Home
15 févr. 2016
Récapitulatif
L'équipe de recherche de la phase 2 de FightAIDS@Home développe et teste de nouvelles façons d'utiliser la grande puissance de calcul du World Community Grid. Leur objectif est de se baser sur les résultats de la phase 1 tout en utilisant les ressources des bénévoles aussi efficacement que possible.
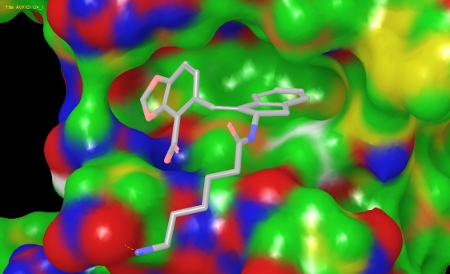
Cette molécule, connue sous le nom AVX101124, a été identifiée dans la phase 1 de FightAIDS@Home comme étant importante pour notre recherche en cours.
Aperçu
Notre équipe FightAIDS@Home - Phase 2 s'acclimate à l'exécution du logiciel de recherche sur cette ressource de calcul encore non conventionnelle et très puissante. Nous analysons les résultats préliminaires des premiers lots de travaux de recherche, qui ont été utilisés pour tester différentes approches de simulation, et rechercher les moyens les plus efficients d'utiliser la grande quantité de temps de calcul donnée. Nous avons également préparé un grand nombre de nouvelles unités de travail tout en réoutillant notre traitement des données et les canaux d'analyse pour faire face à l'afflux massif de résultats.
Utiliser les simulations de Bedam, pour FightAIDS@Home - Phase 2, présente une énorme opportunité d'affiner et d'enrichir les résultats de la phase 1. Cependant, avant d'affiner les résultats identifiés dans la phase 1 et de nouveaux composés étudiés par nos collaborateurs du Centre HIVE, nous avons besoin de développer et tester de nouvelles façons d'exécuter notre logiciel avec les contraintes imposées par l'infrastructure de grille de calcul.
Détails
L'ensemble actuel des travaux de recherche («unités de travail») a été conçu pour répondre à trois objectifs. Tout d'abord, nous évaluons comment notre nouveau schéma de simulation, adapté pour les calculs d'énergie libre à l'aide des ressources distribuées et hétérogènes de World Community Grid, se compare avec les résultats des grappes de serveurs à hautes performances homogènes plus traditionnelles. Nous avons lancé deux ensembles différents de simulations sur World Community Grid qui diffèrent dans la façon dont les paramètres de fonction d'énergie varient entre de nombreuses complexes liaison-protéine cibles simulées. Deuxièmement, les simulations nous permettent de revoir le calcul de l'énergie libre de liaison (scores de liaison) et la prédiction des modes (poses) de liaison pour un ensemble de données bien étudié, dont la protéine intégrase du VIH que nous avons étudiée précédemment dans le défi de prédiction de l'énergie libre de liaison SAMPL4. En effectuant ces différentes simulations, sur cet ensemble de référence de complexes, nous pouvons concevoir et optimiser les futurs lots de simulations afin d'être aussi efficaces que possible en termes de ressources des bénévoles.
La première série de résultats de simulation (expériences 0-52) est presque terminée et a été analysée. Nous prévoyons que ce premier programme de simulation est largement supérieur au deuxième schéma testé dans des expériences 53-105. Nous sommes à environ 60% de ces 106 premières expériences et si l'analyse préliminaire de la deuxième série d'expériences prouve notre hypothèse correctement, nous pourrons choisir de mettre un terme à la deuxième série de simulations avant la fin en vue de passer à de nouveaux lots, tout en utilisant le meilleur programme de simulation.
En outre, alors que vous avez crunché nos unités de travail sans réplication (quorum de 1), nous avons conçu les lots avec une redondance intégrée - ce qui signifie que les travaux de recherche sont affectés plus d'une fois dans le but de comparer les résultats et de confirmer leur exactitude - nous en concluons aujourd'hui que nous avons agi avec trop de prudence. Il ressort de l'analyse de la première série de lots que les protocoles de simulation actuels peuvent être revus à la baisse pour les futurs lots, ce qui permet des simulations concurrentes plus complexes sur le World Community Grid pour avancer. Nous préparons actuellement la prochaine série de lots à partir des résultats d'amarrage de plus grande complexité du défi SAMPL4 que nous avons récemment reçus du laboratoire MGL au Scripps.
Nous prévoyons que cette première année de FightAIDS@Home Phase 2 sera extrêmement enrichissante pour notre groupe et ses collaborateurs au Centre HIVE, et nous sommes très reconnaissants d'avoir eu cette occasion grâce à IBM, et surtout, les bénévoles du World Community Grid.
Cela a été également un mois excitant pour le laboratoire Levy. Nous avons le plaisir d'annoncer que le numéro de Janvier de Protein Science est un numéro spécial en reconnaissance de la contribution de Ronald Levy au domaine de la biophysique informatique! Le numéro est librement accessible en ligne. Le Professeur Ron Levy, qui a conçu l'outil de Bedam utilisé dans cette phase du projet, conduit les simulations moléculaires de la phase 2 et nous sommes très heureux de célébrer ses réalisations dans ce domaine.
article source: http://www.worldcommunitygrid.org/about_us/viewNewsArticle.do?articleId=463


